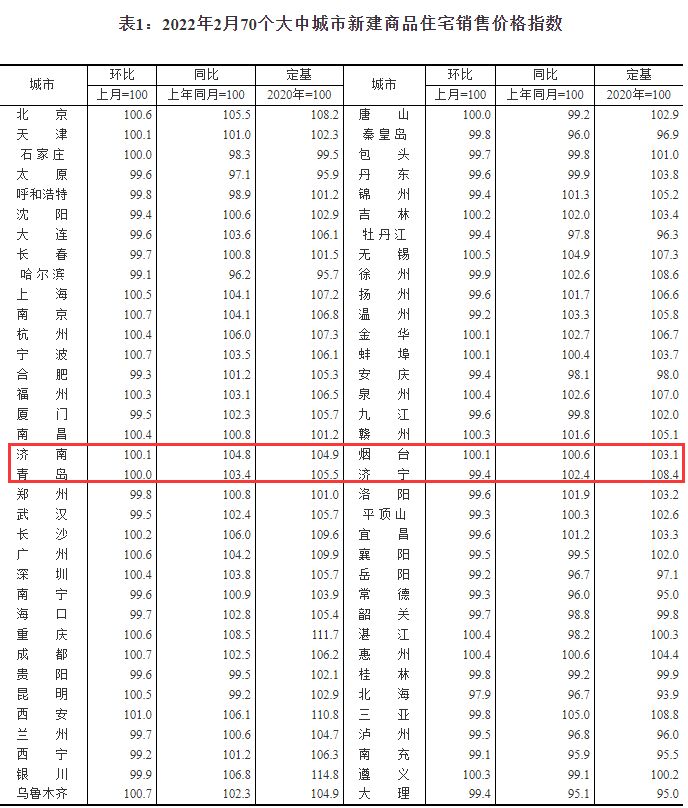
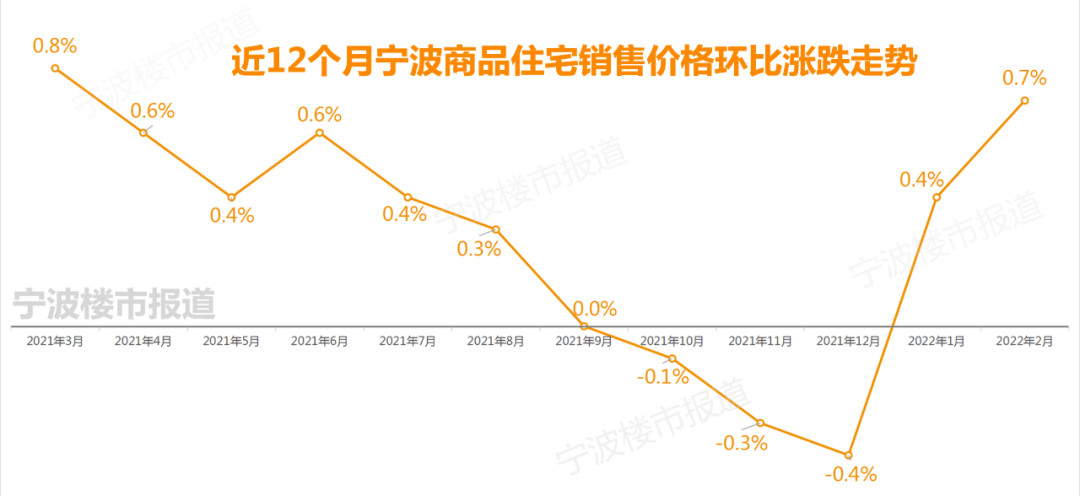
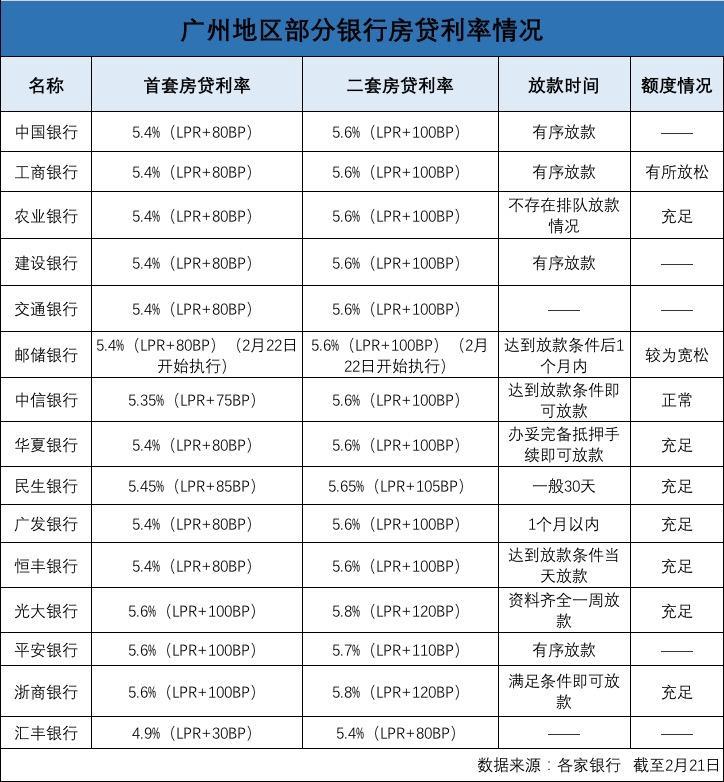
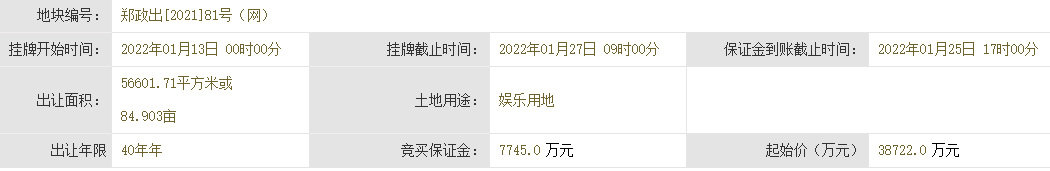
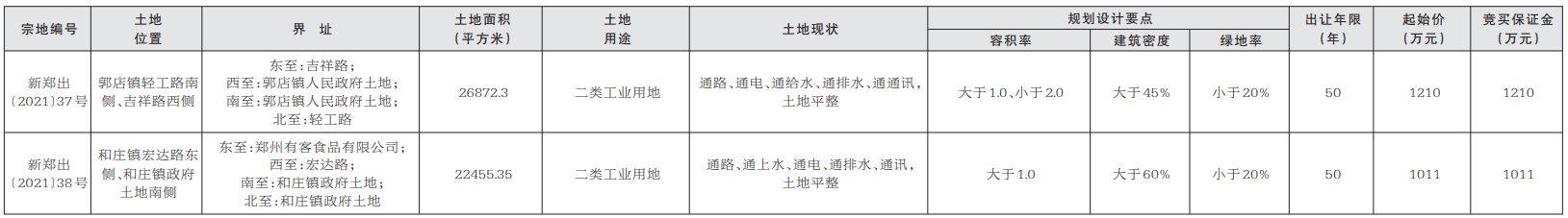
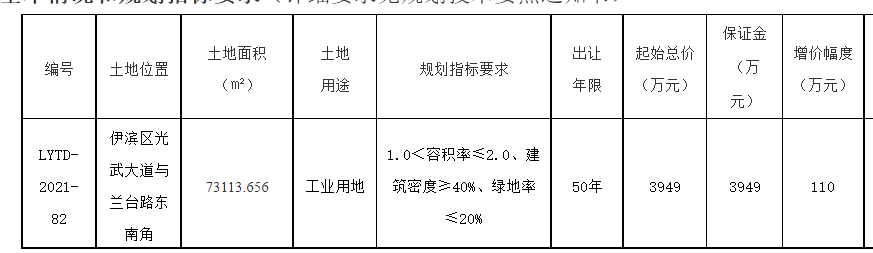
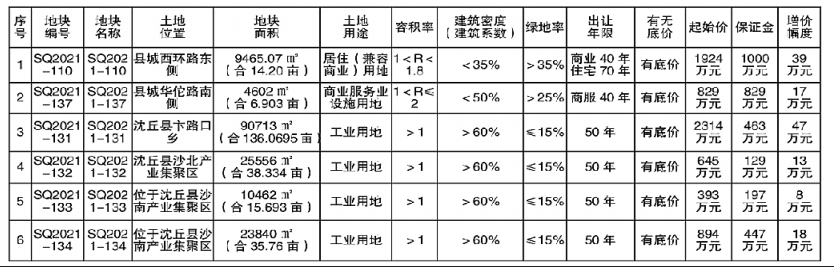
新完成的基因组被称为T2T-CHM13,代表了目前参考基因组的一个重大升级,该基因组被医生用来寻找与疾病有关的突变,以及被研究人类遗传变异进化的科学家使用。
除其他事项外,新的DNA序列揭示了关于着丝粒(centromere)周围区域的前所未有的细节,着丝粒是细胞分裂时染色体被抓取和拉开的地方,确保每个“子”细胞继承正确的染色体数量。这个区域内的变异性也可能为我们的人类祖先如何在非洲进化提供新的证据。
加利福尼亚大学伯克利分校的博士后研究员Nicolas Altemose说:“揭示这些以前缺失的基因组区域的完整序列告诉我们很多关于它们是如何组织起来的,这对于许多染色体来说是完全未知的。”他是四篇关于已完成基因组的新论文的共同作者。“以前,我们只是对那里的情况有最模糊的了解,而现在它已经清晰到了单碱基对的分辨率。”
Altemose是一篇描述着丝粒周围碱基对序列的论文的第一作者。一篇解释如何进行测序的论文出现在4月1日的《科学》杂志印刷版上,而Altemose的着丝粒论文和其他四篇描述新序列告诉我们什么的论文在该杂志上进行了总结,论文全文发布在网上。四篇配套论文,包括Altemose是共同第一作者的一篇,也于4月1日在《自然方法》杂志上在线发表。
测序和分析是由一个由100多人组成的团队完成的,即所谓的“端粒到端粒”联盟(T2T),以覆盖所有染色体末端的端粒命名。该联盟的所有22条常染色体和X性染色体的无间隙版本由30.55亿个碱基对组成,这些碱基对是构建染色体和我们的基因的单位,还有19969个蛋白质编码基因。在蛋白质编码基因中,T2T团队发现了大约2000个新的基因,其中大部分是禁用的,但其中115个可能仍在表达。他们还在人类基因组中发现了大约200万个额外的变体,其中622个发生在医学相关的基因中。
“将来,当某人的基因组被测序时,我们将能够识别他们DNA中的所有变体,并利用这些信息更好地指导他们的医疗保健,”T2T的领导人之一、美国国立卫生研究院国家人类基因组研究所(NHGRI)的高级调查员Adam Phillippy说。“真正完成人类基因组序列就像戴上了一副新眼镜。现在我们可以清楚地看到一切,我们离理解这一切意味着什么又近了一步。”
不断演变的着丝粒
着丝粒内和周围的新DNA序列共占整个基因组的6.2%,即近1.9亿个碱基对,或核苷酸。在剩下的新增加的序列中,大部分被发现在每条染色体末端的端粒周围和核糖体基因周围的区域。整个基因组仅由四种类型的核苷酸组成,这些核苷酸以三组为单位,对用于构建蛋白质的氨基酸进行编码。Altemose的主要研究涉及寻找和探索染色体上蛋白质与DNA相互作用的区域。
Altemose说:“没有蛋白质,DNA就什么都不是。”在获得牛津大学统计学博士学位后,他于2021年在加州大学伯克利分校和旧金山分校联合获得了生物工程博士学位。“DNA是一组指令,如果它周围没有蛋白质来组织它,调节它,在它受损时修复它,并复制它,就没有人可以读懂它。蛋白质与DNA的相互作用确实是基因组调控的所有行动发生的地方,能够绘制出某些蛋白质与基因组结合的位置,对于理解它们的功能真的很重要。”
在T2T联盟对缺失的DNA进行测序后,Altemose和他的团队使用新技术找到了着丝粒内的位置,在那里,一个被称为"动粒"的大蛋白复合物牢固地抓住了染色体,以便细胞核内的其他机器能够将染色体对拉开。
他说:“当这出错时,你最终会出现染色体错误分离的情况,而这将导致各种问题。如果这发生在减数分裂中,这意味着你可能出现染色体异常,导致自发流产或先天性疾病。如果它发生在体细胞中,你可能最终患上癌症--基本上,有大量错误调节的细胞。”
他们在着丝粒内和周围发现的是新的序列层叠在旧的序列层上,就像通过进化,新的着丝粒区域被反复铺设以结合到动粒上。旧区域的特点是有更多的随机突变和缺失,表明它们不再被细胞使用。较新的与动粒结合的序列变化较少,而且甲基化程度也较低。甲基化的增加是一个表观遗传标签,倾向于使基因沉默。
着丝粒内和周围的所有层都是由重复长度的DNA组成的,基于一个大约171个碱基对长的单位,这大约是包裹着一组蛋白质形成核糖体的DNA的长度,保持DNA的包装和紧凑。这些171个碱基对的单位形成了更大的重复结构,被串联重复多次,在着丝粒周围建立了一个大的重复序列区域。
T2T团队只关注一个人类基因组,该基因组是从一个被称为葡萄胎的非癌症肿瘤中获得的,它本质上是一个拒绝母体DNA而复制其父体DNA的人类胚胎。这样的胚胎会死亡并转化为肿瘤。但是这个痣有两个相同的父系DNA副本--都带有父亲的X染色体,而不是来自母亲和父亲的不同DNA--这一事实使它更容易测序。
Altemose说,研究人员本周还发布了一个来自不同来源的Y染色体的完整序列,该序列花费的时间几乎与基因组的其他部分加起来一样长。对这个新的Y染色体序列的分析将出现在未来的出版物中。
Altemose和他的团队,包括加州大学伯克利分校的项目科学家Sasha Langley,还用新的参考基因组作为支架,比较了来自世界各地的1600个个体的中心粒DNA,揭示了着丝粒周围重复DNA的序列和拷贝数的重大差异。以前的研究表明,当古人类群体从非洲迁移到世界其他地方时,他们只带走了一小部分基因变体的样本。Altemose和他的团队证实,这种模式延伸到了着丝粒。
Altemose说:“我们所发现的是,在非洲大陆以外的具有近期血统的个体中,他们的着丝粒,至少在X染色体上,往往分为两个大的集群,而大多数有趣的变异是在具有近期非洲血统的个体中。鉴于我们对基因组其他部分的了解,这并不完全是一个惊喜。但它所表明的是,如果我们想看看这些着丝粒区域的有趣变异,我们确实需要集中精力对更多的非洲基因组进行测序,并进行完整的端粒到端粒的序列组装。”
他指出,着丝粒周围的DNA序列也可以用来追踪人类的血统,追溯到我们共同的猿人祖先。
Altemose说:“当你远离活跃的着丝粒部位时,你会得到越来越多的退化序列,以至于如果你走到这个重复序列‘海洋的最远海岸’,你开始看到古老的着丝粒,也许,我们的灵长类祖先的着丝粒曾经与动粒结合。这几乎就像化石的层次。”
长读测序“改变了游戏规则”
T2T的成功归功于一次对长DNA片段进行测序的改进技术,这有助于确定高度重复的DNA片段的顺序。其中有PacBio的HiFi测序技术,它可以高精度地读取长度超过20,000个碱基对的数据。另一方面, Oxford Nanopore技术有限公司开发的技术可以读取多达几百万个碱基对的序列,尽管保真度较低。作为比较,Illumina公司的所谓下一代测序技术仅限于数百个碱基对。
Altemose说:“这些新的长读DNA测序技术真是令人难以置信;它们是这样的游戏改变者,不仅对于这个重复的DNA世界,而且因为它们允许你对单个长的DNA分子进行测序。你可以开始在一个分辨率水平上提出问题,这在以前是不可能的,即使是短读测序方法也不可能。”
Altemose计划进一步探索着丝粒区域,使用他和斯坦福大学的同事开发的一种改进技术来确定染色体上被蛋白质结合的位置,类似于动粒与着丝粒结合的方式。这项技术也使用了长读测序技术。他和他的小组在本周发表在《自然方法》杂志上的一篇论文中描述了这种技术,称为定向甲基化与长读测序(DiMeLo-seq)。
同时,T2T联盟正在与人类泛基因组参考联盟合作,致力于建立一个代表全人类的参考基因组。
Altemose说:“我们应该有一个代表每个人的参考,而不是仅仅从一个人类个体或一个葡萄胎(甚至不是真正的人类个体)获得一个参考。关于如何实现这一目标,有各种想法。但是我们首先需要的是掌握这种变异是什么样子的,我们需要大量高质量的个体基因组序列来完成这个任务。”
他在着丝粒区域的工作,他称之为"一个激情项目",是由博士后奖学金资助的。T2T项目的负责人是加州大学圣克鲁兹分校的Karen Miga、华盛顿大学的Evan Eichler和NHGRI的Adam Phillippy,后者提供了大部分的资金。加州大学伯克利分校着丝粒论文的其他合著者是生物工程副教授Aaron Streets;分子和细胞生物学教授Abby Dernburg和Gary Karpen;项目科学家Sasha Langley;以及前博士后研究员Gina Caldas。
-
上海昨日新增本土感染者“268+13086”
头条 22-04-05
-
关于郑州市新增1例新冠肺炎无症状感染者的情况通报
头条 22-04-05
-
太康县昨日新增无症状感染者13例,活动轨迹公布
头条 22-04-04
-
多地出台购房优惠鼓励生娃,这一城市拟最高补2万
头条 22-04-04
-
上海今日核酸采样工作顺利完成 还将进行检测复核研判 工作结束前将继续封控
头条 22-04-04
-
20个“最有钱”城市:北上深资金总量均超10万亿
头条 22-04-04
-
安阳市景区、公共文化体育场馆、文化娱乐场所暂停开放
头条 22-04-04
-
115家A股上市公司股息率超5%,释放何种信号?
头条 22-04-04
-
商丘紧急通告:即日起,取消全部宾馆饭店堂食活动
头条 22-04-04
-
中化现代农业河南公司牵手河南远海基金,共建区域标杆农业全产业链体系
头条 22-04-04
-
国家卫健委:昨日新增本土确诊1366例,新增本土无症状11771例
头条 22-04-04
-
鹤壁出台28条硬核举措助力中小企业纾困解难
头条 22-04-04
-
上海昨日新增本土确诊425例,新增本土无症状感染者8581例
头条 22-04-04
-
河南昨日新增本土确诊2例、本土无症状感染者20例
头条 22-04-04
-
郑州新增4例无症状感染者、1例确诊病例,活动轨迹公布
头条 22-04-04
-
今日零时起,河南启用来(返)豫人员报备系统
头条 22-04-04
-
设研院大数据“撑腰”,百吨“巨无霸”从郑州运抵武汉
头条 22-04-03
-
河南桐柏发现自然界新矿物——空铁黝银矿
头条 22-04-03
-
比亚迪宣布停止燃油汽车整车生产
头条 22-04-03
-
比亚迪:3月新能源汽车销量为104878辆 同比增长422.97%
头条 22-04-03
-
安伟调研督导新冠肺炎定点救治医院改建工作
头条 22-04-03
-
中国职业足球俱乐部欠薪解决方案公布
头条 22-04-03
-
安阳滑县发现1例新冠肺炎确诊病例
头条 22-04-03
-
河南这些项目入选!2022年农业产业融合发展项目创建名单公示
头条 22-04-03
-
华之源生物:金融创新为河南科研项目发展破局
头条 22-04-03
-
科创金融助力,河南联合精密发力精细研磨技术 打破国际技术垄断
头条 22-04-03
-
张伯礼谈此轮疫情:应该坚定抗疫信心
头条 22-04-03
-
何雄会见中国铁建中原区域总部副总经理贾筱煜
头条 22-04-03
-
河南昨日新增本土无症状感染者20例
头条 22-04-03
-
国家卫健委:昨日新增本土“1455+11691”例
头条 22-04-03
-
周口太康县新增11例无症状感染者 活动轨迹公布
头条 22-04-03
-
立方风控鸟·晚报(4月2日)
头条 22-04-02
-
梦想日近,新能源汽车下半场要防过热 | 立方快评
头条 22-04-02
-
UU跑腿张茗淳:未来将继续坚持直接融资与间接融资并重
头条 22-04-02
-
河南对小微企业顶格执行“六税两费”减免政策
头条 22-04-02
-
郑州新增1例无症状感染者 活动轨迹公布
头条 22-04-02
-
猪价向下、饲料向上,猪企如何“夹缝生存”
头条 22-04-02
-
自贸区郑州片区法院搭建首家5G法庭便民服务站
头条 22-04-02
-
全国首个!河南省地方政策性科创金融运营启动,郑州银行科创金融事业部、金融智谷支行揭牌 | 极刻
头条 22-04-02
-
不缺钱为何上市?万科分拆万物云赴港IPO,拟募资投向这些领域
头条 22-04-02
-
数字人民币试点城市扩容!天津、重庆、广州、福州、厦门等入围
头条 22-04-02
-
明日起郑州家电以旧换新部分规则调整,平板电脑不在补贴范围
头条 22-04-02
-
河南省地方政策性科创金融运营启动暨郑州银行科创金融事业部和金融智谷支行揭牌仪式举行
头条 22-04-02
-
交易商协会进一步推出适用于2022年当年的会费减免措施
头条 22-04-02
-
总投资超544亿元!河南批复4条高速公路 途经这些地方
头条 22-04-02
-
河南省高等教育自学考试延期举行
头条 22-04-02
-
今日17时起,郑州地铁实施“双码”进站
头条 22-04-02
-
蒋凡卸任淘宝法定代表人及董事长
头条 22-04-02
-
浙江衢州取消限购政策
头条 22-04-02
-
国家卫健委:坚决遏制疫情扩散,确保如期实现“社会面清零”目标
头条 22-04-02
-
1288万已拨付!河南首次试行省重大科技专项经费“直通车”制度
头条 22-04-02
-
63家典当行、保理、融租!河南省金融局2022年执法检查名单公布
头条 22-04-02
-
约6.7亿元!开封东南片区将有大动作!
头条 22-04-02
-
楼阳生为郑州银行科创金融事业部和金融智谷支行揭牌
头条 22-04-02
-
长春疫情与农贸市场、工地等聚集性疫情并引发社区感染有关
头条 22-04-02
- 科学家们公布完整的人类基因组序列 并揭示2022-04-05
- "醉猴"实地研究证实灵长类动物对酒精类水果2022-04-05
- 哈勃太空望远镜发现一个蛇形的螺旋星系:NG2022-04-05
- 6日起郑州一区域局部降压供水11天,两路段2022-04-05
- NASA的Artemis I任务湿式排练测试预计将于2022-04-05
- 文化“卷王”来了 《清明奇妙游》再出爆款2022-04-05
- 4月4日河南新增本土无症状感染者31例2022-04-05
- 水星的神秘历史:竟然真的有水 而且还很多2022-04-05
- 科学家利用光在固体材料中设计量子态2022-04-05
- 新研发的DNA纳米技术有望将疫苗和医药的开2022-04-05
- 晴天霸屏 气温波动回升,节后河南将冲击30℃2022-04-05
- 科学家设计出一种能清除肾结石最小碎片的水2022-04-05
- 这个清明小长假 公园赏花、郊区野营成为郑2022-04-05
- 多部电影撤档 清明档郑州电影市场略显冷清2022-04-05
- 河南便民办税再升级 分两批推出105条便民2022-04-05
- 《清明奇妙游》中的西园雅集:千年后我们仍2022-04-05
- 石家庄市元氏县新增1例新冠肺炎无症状感染2022-04-05
- 山西省洪洞县确诊1名新冠肺炎输入病例,系2022-04-05
- 河南省昨日新增本土无症状感染者31例2022-04-05
- 山东济南新增本土确诊9例,本土无症状1例,2022-04-05
- 广西昨日新增本土确诊病例2例 均在百色市2022-04-05
- 冷空气影响北方地区 西藏东部云南四川等地2022-04-05
- 海南昨日新增1例本土确诊病例和1例本土无症2022-04-05
- 4月4日0-24时,湖北新增本土无症状感染者16例2022-04-05
- 保障“菜篮子” 海口常年蔬菜基地抓生产保2022-04-05
- 最高气温直冲30℃?送走清明假期 升温愈演2022-04-05
- 驰援上海,甘肃来了2022-04-05
- 闽江航运集散两用货船开建2022-04-05
- 安徽省财贸轻纺烟草工会开展就业援助:线上2022-04-05
- 上海昨日新增本土感染者“268+13086”2022-04-05